MOESAN
Elite member
- Messages
- 5,885
- Reaction score
- 1,294
- Points
- 113
- Location
- Brittany
- Ethnic group
- more celtic
- Y-DNA haplogroup
- R1b - L21/S145*
- mtDNA haplogroup
- H3c
here something interesting (very!) but in french (to begin)
mardi, septembre 9 2014
[h=2]Structure génétique à petite échelle dans l'ouest de la France[/h] Par bernard secher le mardi, septembre 9 2014, 21:50 - Génétique des populations
Ce papier de Matilde Karakachoff est intéressant: Fine-scale human genetic structure in Western France.
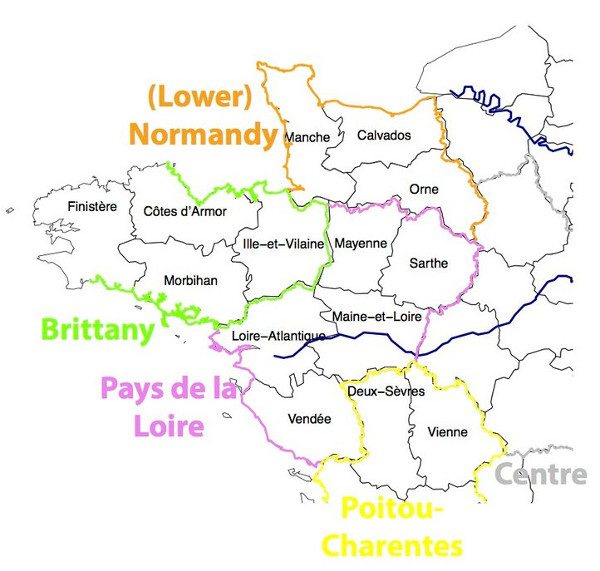
Dans cette étude, 1684 échantillons de l'ouest de la France ont été testés sur leur ADN autosomal sur 377 566 SNPs, afin d'effectuer une analyse de la structure génétique à petite échelle. Cette étude est limitée aux anciennes régions de Bretagne, Anjou, Poitou, Maine et Basse Normandie correspondant aux départements actuels suivants: Calvados, Côtes-d’Armor, Finistère, Ille-et-Vilaine, Loire-Atlantique, Maine-et-Loire, Manche, Mayenne, Morbihan, Orne, Sarthe, Deux-Sèvres, Vendée et Vienne:
Pour étudier la structure génétique, les auteurs ont utilisé le logiciel ADMIXTURE avec des valeurs de coefficient K=2 et K=3. La valeur de K=2 permet de séparer les échantillons bretons des autres, et la valeur de K=3 permet de séparer en plus des bretons les échantillons de la Vendée et du sud du Maine-et-Loire:
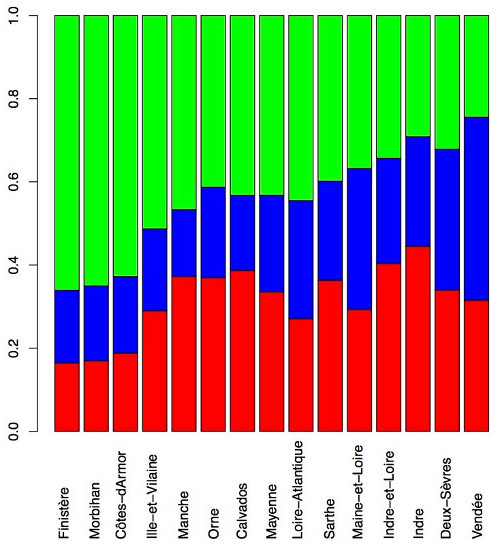
Dans la figure ci-dessus, la composante bretonne est en vert et la composante vendéenne est en bleu. La composante bretonne est maximale dans le Finistère, le Morbihan et les Côtes-d'Armor. La composante vendéenne apparait clairement en bleu dans le schéma ci-dessous:
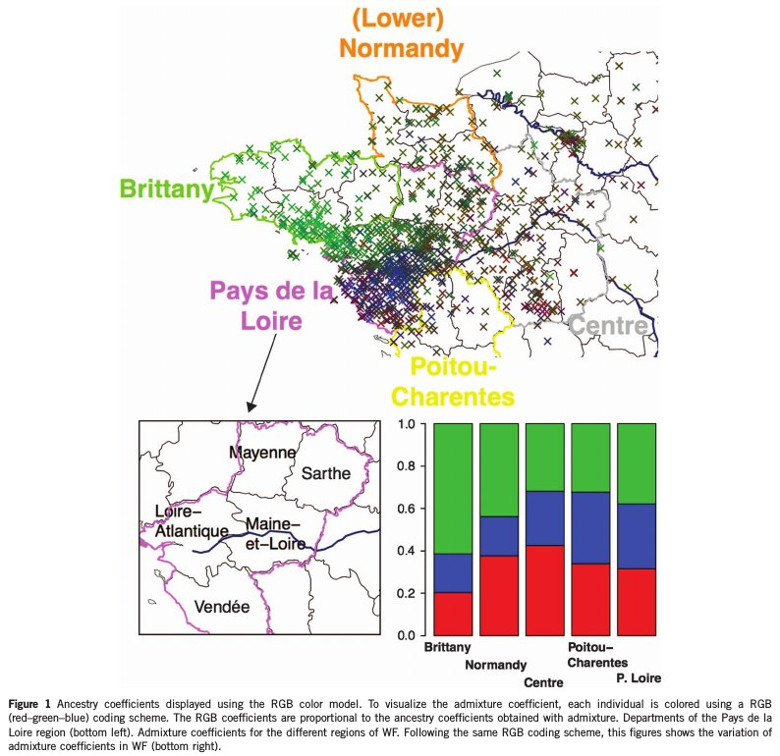
Une Analyse en Composantes Principales permet de confirmer ce résultat:
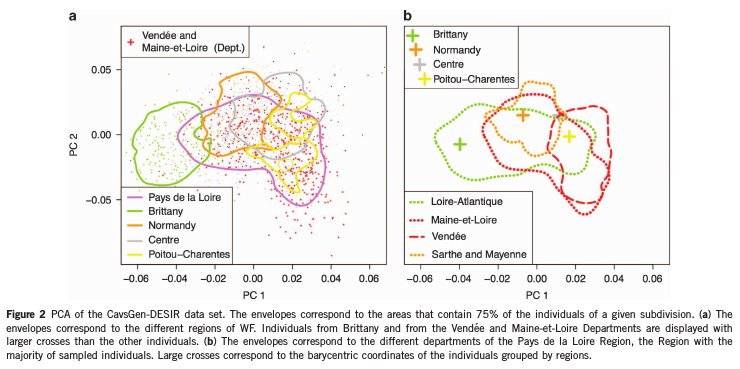
Le schéma ci-dessus à gauche, montre que la première composante permet de séparer les échantillons bretons (en vert), et la seconde composante permet de séparer certains échantillons vendéens. Ensuite une Analyse a été faite uniquement sur la région Pays-de-la-Loire. Une structure génétique apparait dans cette région dans le schéma ci-dessus à droite.
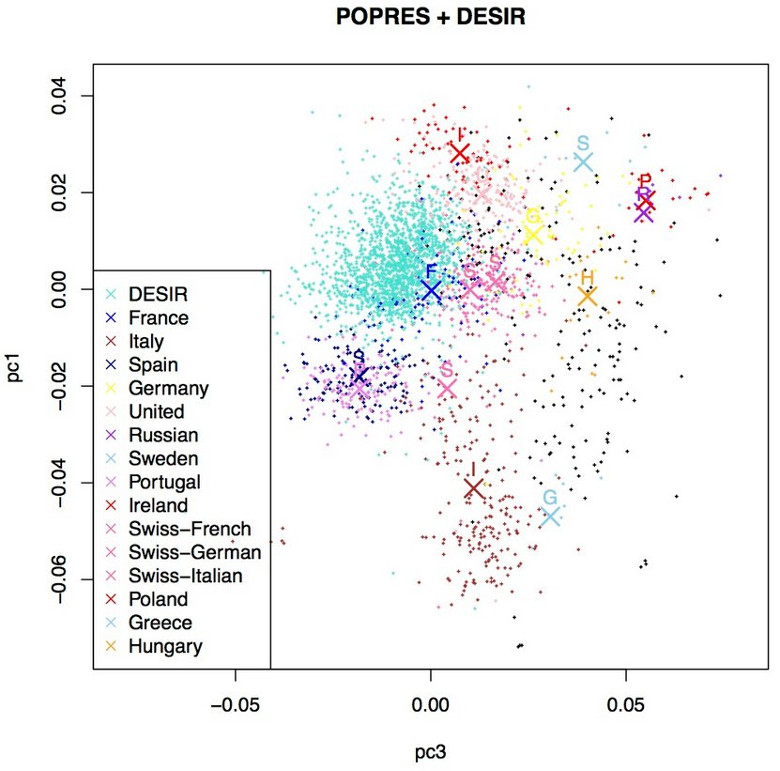
Ensuite ces échantillons ont été comparés avec des populations européennes. Le schéma ci-dessous représentent les composantes PC1 et PC3. Les échantillons de cette étude sont labellisés DESIR (en turquoise). Ils se rapprochent le plus des échantillons du Royaume-Uni, d'Irlande, d'Espagne, de la région francophone de la Suisse et de France:
Ensuite chaque échantillon de l'ouest de la France a été comparé avec chaque échantillon des populations européennes. Pour cela on regarde quels sont les segments d'ADN communs dans chaque paire d'individus. Si ces segments communs entre 2 individus ne sont pas hérités d'un ancêtre commun, on dit que la séquence est identique par état (IBS en anglais). Ainsi les populations les plus proches de la population de l'ouest de la France sont les populations de France, du Royaume-Uni et d'Irlande comme le montre la figure ci-dessous:
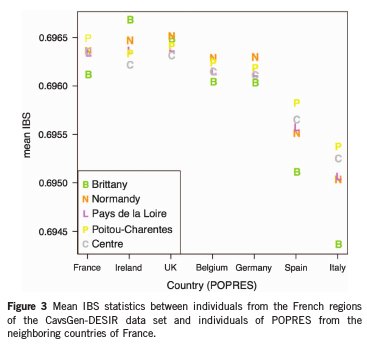
Quand on les compare avec les autres régions de l'ouest de la France, les Bretons ont une affinité plus importante avec les Irlandais et plus faible avec les espagnols et les italiens.
Les auteurs ont ensuite regardé quelles sont les régions du génome plus spécifiques aux Bretons. Ils ont ainsi remarqué que les Bretons sont reliés au gène qui donne une tolérance au lactose, situé dans le chromosome 2 (rs6754311 et rs4988235), et au complexe HLA situé sur le chromosome 6. Pour ces deux régions, la distance génétique entre les Bretons et les Irlandais est faible.
Cette étude a donc permis de mettre en évidence une structure génétique à petite échelle dans l'ouest de la France avec la détection d'une ascendance liée aux Bretons et une autre aux Vendéens. Ces résultats suggèrent une isolation par distance des Bretons. La plus grande distance génétique mesurée à une distance de 30 km chez les Bretons est liée à une dérive génétique dans une population moins nombreuse dans cette région. Cette grande distance génétique chez les Vendéens est liée à la présence d'individus avec une ascendance spécifique. La proximité génétique des Bretons et des Irlandais se retrouve également dans les haplogroupes du chromosome Y, reflétant probablement une origine commune.
mardi, septembre 9 2014
[h=2]Structure génétique à petite échelle dans l'ouest de la France[/h] Par bernard secher le mardi, septembre 9 2014, 21:50 - Génétique des populations
Ce papier de Matilde Karakachoff est intéressant: Fine-scale human genetic structure in Western France.
Dans cette étude, 1684 échantillons de l'ouest de la France ont été testés sur leur ADN autosomal sur 377 566 SNPs, afin d'effectuer une analyse de la structure génétique à petite échelle. Cette étude est limitée aux anciennes régions de Bretagne, Anjou, Poitou, Maine et Basse Normandie correspondant aux départements actuels suivants: Calvados, Côtes-d’Armor, Finistère, Ille-et-Vilaine, Loire-Atlantique, Maine-et-Loire, Manche, Mayenne, Morbihan, Orne, Sarthe, Deux-Sèvres, Vendée et Vienne:

Pour étudier la structure génétique, les auteurs ont utilisé le logiciel ADMIXTURE avec des valeurs de coefficient K=2 et K=3. La valeur de K=2 permet de séparer les échantillons bretons des autres, et la valeur de K=3 permet de séparer en plus des bretons les échantillons de la Vendée et du sud du Maine-et-Loire:

Dans la figure ci-dessus, la composante bretonne est en vert et la composante vendéenne est en bleu. La composante bretonne est maximale dans le Finistère, le Morbihan et les Côtes-d'Armor. La composante vendéenne apparait clairement en bleu dans le schéma ci-dessous:

Une Analyse en Composantes Principales permet de confirmer ce résultat:

Le schéma ci-dessus à gauche, montre que la première composante permet de séparer les échantillons bretons (en vert), et la seconde composante permet de séparer certains échantillons vendéens. Ensuite une Analyse a été faite uniquement sur la région Pays-de-la-Loire. Une structure génétique apparait dans cette région dans le schéma ci-dessus à droite.
Ensuite ces échantillons ont été comparés avec des populations européennes. Le schéma ci-dessous représentent les composantes PC1 et PC3. Les échantillons de cette étude sont labellisés DESIR (en turquoise). Ils se rapprochent le plus des échantillons du Royaume-Uni, d'Irlande, d'Espagne, de la région francophone de la Suisse et de France:

Ensuite chaque échantillon de l'ouest de la France a été comparé avec chaque échantillon des populations européennes. Pour cela on regarde quels sont les segments d'ADN communs dans chaque paire d'individus. Si ces segments communs entre 2 individus ne sont pas hérités d'un ancêtre commun, on dit que la séquence est identique par état (IBS en anglais). Ainsi les populations les plus proches de la population de l'ouest de la France sont les populations de France, du Royaume-Uni et d'Irlande comme le montre la figure ci-dessous:

Quand on les compare avec les autres régions de l'ouest de la France, les Bretons ont une affinité plus importante avec les Irlandais et plus faible avec les espagnols et les italiens.
Les auteurs ont ensuite regardé quelles sont les régions du génome plus spécifiques aux Bretons. Ils ont ainsi remarqué que les Bretons sont reliés au gène qui donne une tolérance au lactose, situé dans le chromosome 2 (rs6754311 et rs4988235), et au complexe HLA situé sur le chromosome 6. Pour ces deux régions, la distance génétique entre les Bretons et les Irlandais est faible.
Cette étude a donc permis de mettre en évidence une structure génétique à petite échelle dans l'ouest de la France avec la détection d'une ascendance liée aux Bretons et une autre aux Vendéens. Ces résultats suggèrent une isolation par distance des Bretons. La plus grande distance génétique mesurée à une distance de 30 km chez les Bretons est liée à une dérive génétique dans une population moins nombreuse dans cette région. Cette grande distance génétique chez les Vendéens est liée à la présence d'individus avec une ascendance spécifique. La proximité génétique des Bretons et des Irlandais se retrouve également dans les haplogroupes du chromosome Y, reflétant probablement une origine commune.